За да се постигнат поставените цели екипът на проекта прилага разнообразни изследователски методи, похвати и техники: биоинформатични и геномни проучвания, АСО технология, in vitro експерименти, микробиологични методи, клетъчно-биологични и други анализи. Научният проект може да бъде разделен мисловно на 4 отделни части. Първата включва биоинформатични и геномни проучвания с ключово търсене S. pneumoniae, позволяващи да изберем подходящи мишени. През втория етап провеждаме геномни проучвания, АСО технологията и дизайна на АСО. Третият етап е фокусиран върху приложението на микробиологичните и синтетично биологичните лабораторни практики, по време на които ще наблюдаваме ефекта на всеки един АСО върху макролидно-резистентни щамове на бактерията. Четвъртият етап е посветен на цитологичните анализи и по-специфично проверка на цитотоксичността, която може да покаже всеки един от АСО. Първата част от нашите фундаментални проучвания е пряко свързана с избора на мишени от бактериалния геном. Първо проучваме условията при които бактерията се развива, специфики на нейните метаболитни процеси, характеристики и особености за методите, чрез които е развила нечувствителност към групи антибиотици в бази данни: RSwitch, NCBI – Gene, Genome, Nucleоtide, Protein, Gene Bank, Rfam, Pfam, KEGG и други). Събираме информация и генерираме текстови FASTA файлове, съдържащи последователности на иРНК и рибопревключватели при макролидно-резистентни щамове от бактерията. Именно тях ще подложим на геномни анализи: Clustal X и множествено подравняване за откриване на мотиви от рибопревключвателите , които са застъпени при различните щамове на бактерията. Ръководителят на проекта, заедно с проф. д-р Роберт Пенчовски създават стратегия за рационален избор на мишени от бактериалния геном, посредством редица проучвания, чиито отговори помагат всяка една мишена да се класифицира като подходяща, много подходяща, най-подходяща или неподходяща. Системата включва 4 основни критерия: разпостранение на рибопревключвателя, биосинтеза на основни метаболити за бактерията, наличието или отсъствието на транспорт през мембраната на същия ключов метаболит и дали транспортът му е под контрола на рибопревключвателя [11]. Биоинформатичното търсене на информация за метаболизма на Streptococcus pneumoniae и важните за нея метаболити става ясно, че се откриват 6 различни класа рибопревкюлчватели. Ще извършим анализ на метаболитните процеси, в които участват рибопревключвателите с цел проверка за пригодността на мишената и избор къде метаболитният път да бъде блокиран – дали те участват в генната регулация и последващия синтез на ключови метаболити за бактерията и дали е наличен транспорт отвън през мембраната и кой го регулера. Ще генерираме Fasta файлове с нуклеотидни последователности рибопревключвателите при бактерия, които ще подложим на Clustal анализ и ще определим мотивите от мишените. Те имат дължина от 12 до 26 нуклеотида, като оптимално е да бъдат от 16 до 22 нуклеотида. След избора на мотив, пристъпваме към Blasic Local Alignment Searching Tool (BLAST) анализ за проверка на наличието на мотивите в човешкия геном. Този анализ ни позволява да определим дали мотивът от нашата мишена се открива и при пробиотичните бактерии или пък при други патогенни бактерии. Така знаем дали е безопасно да насочим антибактериален агент към мотива и кои организми ще бъдат засегнати от него. За да използваме избраните мотиви като основа за скелета при дизайна на АСО е необходимо да генерираме обратно комплементарни последователности в RevComOligo от софтуерния пакет достъпен тук: https://penchovsky.atwebpages.com/applications.php?page=41. Така плавно преминаваме към геномните анализи, които включват изчисляването на минималната свободна енергия и др. показатели с Vienna RNA fold, позволяващи ни да проследим поведението на мотива и да изключим възможността той да се самонагъне. Биоинформатичните анализи на бази данни не са приключили.
Вторият етап е свързан с геномните проучвания, АСО технологията и прецизния компютърен дизайна на АСО, за който отново имаме постулиран модел. Той съдържа пет критерия и се основава на геномен анализ в международни бази данни (NCBI, Gene, GenBank, Rfam, Pfam, KEGG pathway и др.), Clustal X множествени подравнявания на аптамерната част на рибопревключвателя и избор на подходящ мотив.
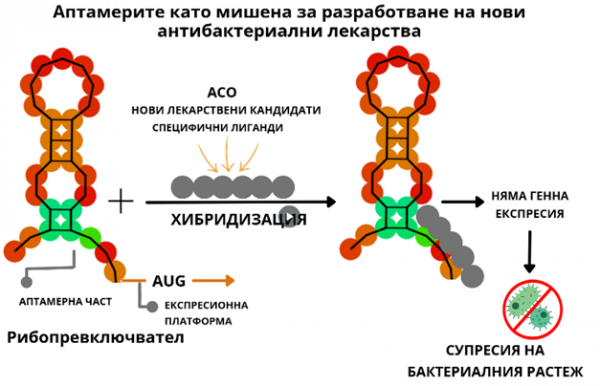
Фигура 1. Схематична структура на рибопревключвател се състои от аптамерен домейн и експресионна платформа. Аптамерната част е чувствителна и се свързва със специфични метаболити, нови лекарствени кандидати и антисенс олигонуклеотиди (АСО). След хибридизация с АСО, структурата е нарушена и генната експресия не е наблюдавана. В резултат на тази регулация, бактериалният растеж е потиснат.
BLAST анализът на мотивите в човешкия геном, както и в геномите на пробиотични и други патогенни бактерии, последван от RevComOligo (https://penchovsky.atwebpages.com/applications) и RNA fold анализ (MFE и PF), са ключова междинна част от процеса. Последната стъпка от дизайна включва модифициране на нуклеотидите и планиране на място на свързване с клетъчно-проникващ пептид. Тази последна стъпка осигурява стабилността на АСОи способността му да се насочва специфично към мишена от генома на S. pneumoniae. През третият етап ще проведем лабораторни изследвания за да установим ефектът на АСО срещу бактерията, посредством наблюдение на клетъчния растеж. Вече синтезирани АСО ще бъдат тествани в изолати на патогенната бактерия. Бактерията се култивира в богати течни и твърди хранителни среди в присъствието и в отсъствието на АСО, за да се установи ефекта им. Тези експерименти плавно преминават към четвъртия етап, в който всяко АСО ще бъде тествано за цитотоксичен ефект, а клетъчните линии на бъбречни клетки. Ще се извърши и фруоресцентна микроскопия.